对于生信论文,目前大趋势是生信筛选+生信验证+湿实验验证。但是,芒果在查阅论文的时候发现,好多杂志其实也在收生信验证的论文。当然,湿实验验证是绝对的加分项,其实也是科研逻辑上的严谨。分析角度仍然符合以前的分析套路,大多数我们在公众号分享过。以下杂志已明确不再接受纯生信,白屏黑字(定期更新)。
1.OncoImmunology
The members of the Editorial Board of OncoImmunology who read your paper found that your work is a purely bioinformatics analysis based on published omics data without any experimental validation or exploration. Your paper did not receive a priority score high enough to justify its in-depth evaluation by peer review.
2. Frontiers in Oncology

Most notably, manuscripts consisting solely of bioinformatics, computational analysis, or predictions of public databases which are not accompanied by validation (independent cohort or biological validation in vitro or in vivo) will not be accepted in any of the sections of Frontiers in Oncology.
3.Cancer Cell International
Cancer Cell International publishes articles on all aspects of cancer cell biology originating from work using laboratory experimentation. The journal focuses on novel cancer studies reporting data from biological experiments performed on cells grown in vitro, in two- or three-dimensional systems, and/or in vivo (animal experiments).
差异表达 (differential expression)+湿实验验证;
生存分析 (survial analysis);
相关分析 (correlation analysis);
统计分析 (statistical analysis);
组学分析 (genomic alterations);
免疫分析 (tumor infiltration analysis);
富集分析(enrichment analysis)。
第80篇生信论文。或许是因为对于Frontiers期刊的深度认可,芒果一直觉得Frontiers众多子刊都是生信投稿的首选。尽管不接收单纯生信的文章,但是对于湿实验验证的生信论文,期刊还是相对友好的。比如今天我们分享的论文,2021年05月28日新近发表在Frontiers in Oncology上。

论文仍然以生信分析为主,仅有简单的细胞系和标本湿实验验证。从方法和材料比较起来,就多了细胞系和细胞培养,RNA抽提和qRT-PCR,以及免疫组化(IHC)。

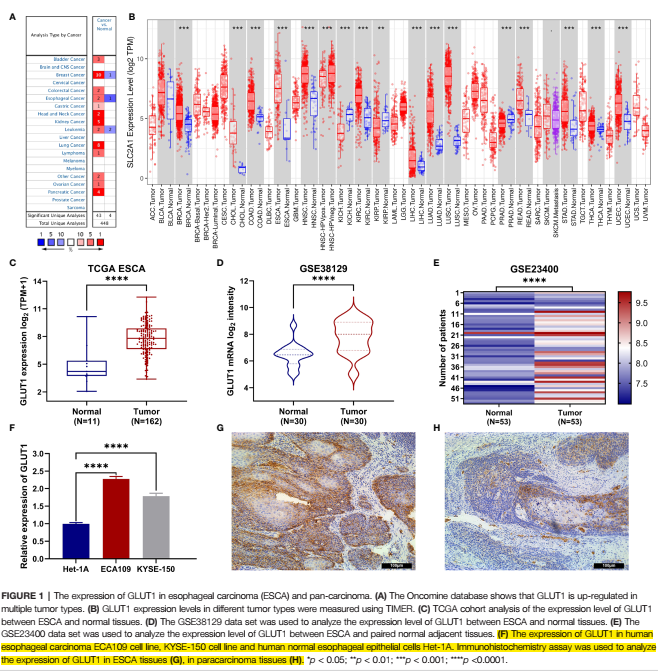
首先,文章聚焦差异表达的分析,从oncomine,TIMER到TCGA和GEO数据,再加上细胞系转录水平(Fig1F)和蛋白水平(Fig1G、H)的验证。一年前,仅有网页数据库分析即可,现在门槛提高了,R语言和湿实验已经逐渐成为必备的验证。
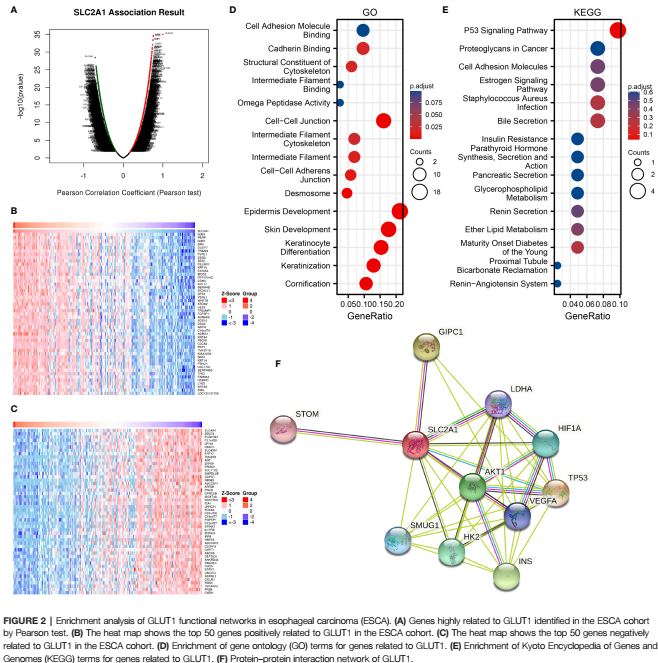
接下来,作者做了差异分析,筛选肝癌中与GLUT1基因密切相关的hub genes;然后用GO分析、KEGG分析、互作分析和热图展示出相关基因。
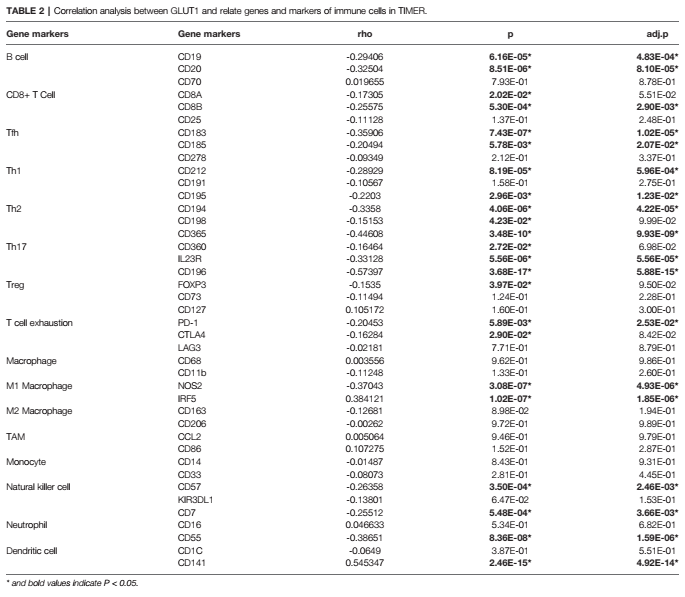
免疫分析,TIMER数据库展示GLUT1与肿瘤浸润淋巴细胞的关系。这些分析还是纯网页数据库完成的,也没有实验验证,相对简单。

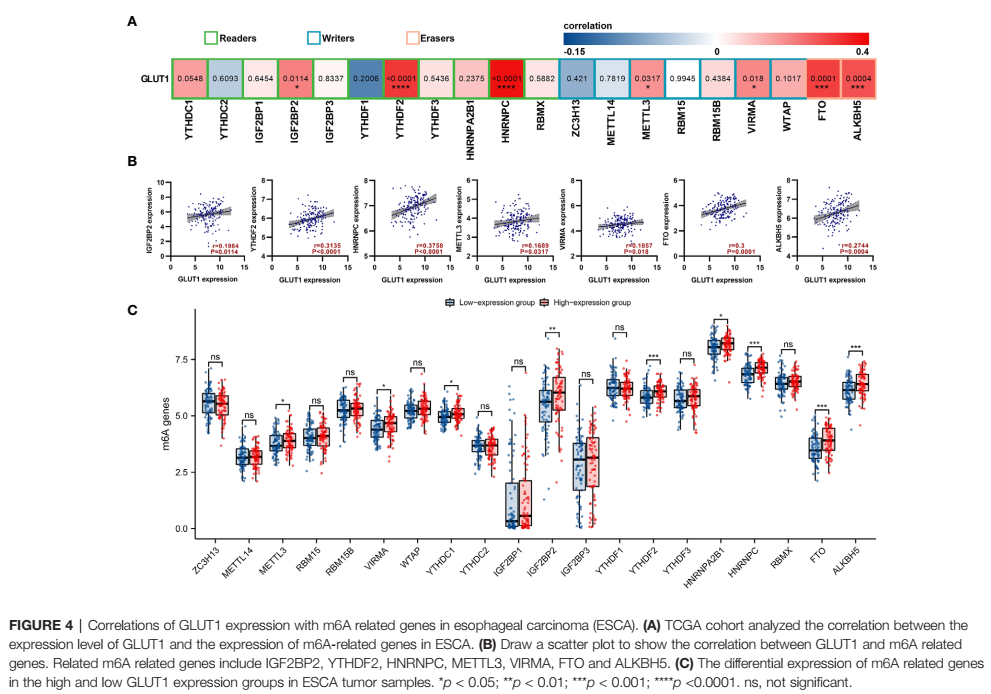
m6A甲基化还跟生信分析联系在一起了,最近特别火,有很多论文出来。We analyzed the TCGA ESCA data set to study the correlation between the expression of GLUT1 and 20 m6A-related genes in ESCA。这20个m6A相关基因也可以被用来做我们自己的分析(Fig4A)。
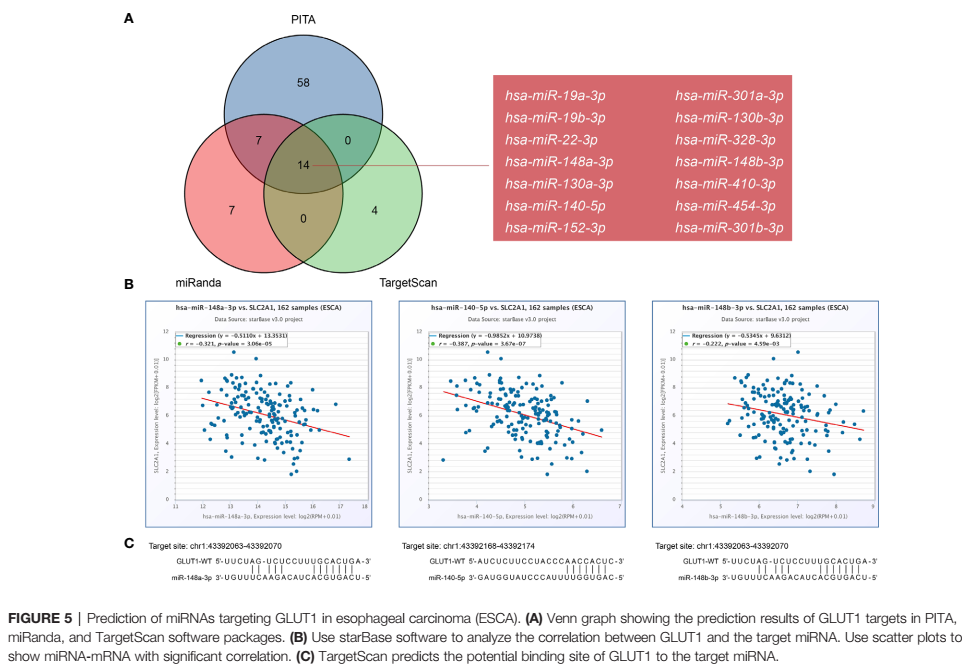
在食管癌中以GLUT1为靶标的miRNA、lncRNA和ceRNA预测,以数据库分析为主。与其他生信论文相比,m6A相关基因和RNA预测分析是该论文较新颖的地方吧,起码文章维度多,显示分析丰富饱满。
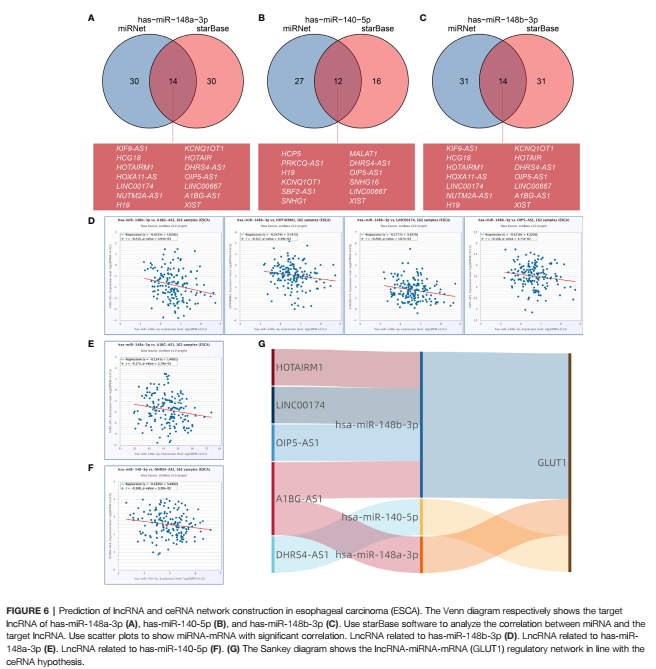
整体来说,文章逻辑上比较明确,差异表发分析,筛选关键基因和相关基因,做免疫分析,相关分析(m6A相关基因,不是病理分析或者免疫检查点相关基因)和miRNA、lncRNA和ceRNA预测。差异表达上有湿实验的验证。但是,文章也有不足,最起码芒果看来就不够好。第一缺少流程图,第二缺少生存分析的内容,补充数据和正文中都没有涉及,尤其是第二条简直不能忍受。如果我是审稿专家,这个问题是一定要回答的。我们自己在做分析的时候,其实也要注意这些点。
一起成长,共同进步,愿果友们多发论文。